�ǽ�������
![]() bioinformatics 2011ǯ05��07��(��) 21:22:24����
bioinformatics 2011ǯ05��07��(��) 21:22:24����
FrontPage-Cytoscape-Tutorials
�Ρ��ɤ�°���ϰʲ����ͤˤʤ�ޤ���
���饤�ɥ��硼 Filtering and Editing in Cytoscape (15 ʬ)
�ϥ�ɥ����� Filtering_and_Editing_in_Cytoscape.pdf (5 �ڡ���)
���塼�ȥꥢ��Υ����� Cytoscape Wiki
���塼�ȥꥢ��Υ���졼���� Kristina Hanspers
���Υ��塼�ȥꥢ��Ǥ�Cytoscape�Τ����Ĥ��α��Ѥ�Ҳ𤷤ޤ���
�ϥ�ɥ����� Filtering_and_Editing_in_Cytoscape.pdf (5 �ڡ���)
���塼�ȥꥢ��Υ����� Cytoscape Wiki
���塼�ȥꥢ��Υ���졼���� Kristina Hanspers
�ܼ�
1 ������
2 �ͥåȥ����°�����ɤ߹���
3 �ե��륿��������
4 �Խ�
���Υ��塼�ȥꥢ��Ǥ�Cytoscape�Τ����Ĥ��α��Ѥ�Ҳ𤷤ޤ���
- �ե��륿��Ŭ�Ѥ��ƿ��������㤤���å������ޤ���
- Cytoscape�Υ���ե��ǥ������Ѥ��ƴ���Ū���Խ���Ԥ��ޤ���
���Υ��塼�ȥꥢ��Ǥϰʲ��Υץ饰����ȥǡ������åȤ��ޤ���
- Institute for Systems Biology��Rowan Christmas������Network Filter�ץ饰����
- RUAL.subset.sif��2005 Oct 20 in Rual et al., Nature 437(7062):1173-8�˥ҥ���ߺ��ѥǡ������åȤȤ���ȯɽ���줿��Τΰ����Ǥ���Cytoscape�������Ѳ�ǽ�Ǥ���
- °�����å�RUAL.na��Ʊ�������Ȥ������Ѳ�ǽ�Ǥ���
- Cytoscape�Ϥ��ޤ���Cytoscape�Υ���������ɤȥ��ȡ���ξܺ٤�Getting Started���������Ť����塼�ȥꥢ��ؤΥ�ȤʤäƤ��ޤ��ˤȤΤ��ȡ�
- Cytoscape��File��˥塼����Import �� Network (Multiple file types)...������ʬ�ǥ���������ɤ����ե�����ѥ�����ꤷ��RUAL.subset.sif�ͥåȥ���ե�������ɤ߹��ߤޤ���
- File �� Import �� Node Attributes...����Ρ��ɤ�°��RUAL.na�ե�������ɤ߹��ߤޤ���
- yFiles organic �쥤�����Ȥ�ͥåȥ����Ŭ�Ѥ��ޤ���

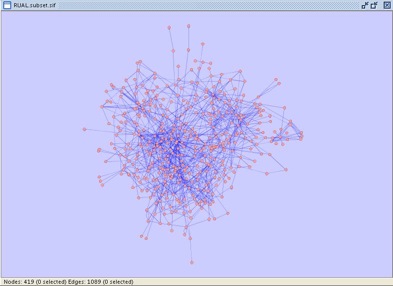
�Ρ��ɤ�°���ϰʲ����ͤˤʤ�ޤ���
- �Ρ���°���ե�����ǥ��ե������Ρ���̾�Ȥ����ɤ߹������Τϥ��ե������ȸƤӤޤ�������°����ɤ����ꤵ��Ƥ��뤫��RUAL.na�ե���������ʻȤ��ƥ����ȥ��ǥ����dz����ƤߤƤ���������
- Cytoscape�ǥ����ȥåפǤϡ�Node Attribute Browser�ˤơ�Select Attributes
 �ܥ����å����ƤߤƤ���������
�ܥ����å����ƤߤƤ��������� - Official HUGO Symbol��̾�դ���줿°�������ܤ��Ƥ����������ޥ����κ��ܥ���ǥ���å����Ƥ���������
- �ޥ����α��ܥ���ǥ�˥塼������ޤ���
- Node Attribute Browser��2�Ĥ�����ޤ���1�Ĥϥ�٥뤬ID�ȤʤäƤ��ư�����Official HUGO Symbol�ȤʤäƤ��ޤ���Cytoscape canvas�Ǥ����Ĥ��ΥΡ��ɤ����ƤߤƤ��������������Ρ��ɤ�ID�ʤ�����Ǥ�Entrez gene ID�ˤȥ��ե������ʰ�����̾��ɽ������ޤ���
���ʤ��ΰ����ͥåȥ���ˤϤ��������ʥ����פΥ��å����ޤޤ�Ƥ��ޤ���Y2H yeast two-hybrid interactions��coAP GST pull-down interactions��three types of literature-based interactions����������������ˤĤ졧non-core��core��hypercore�Ȥʤ�ޤ���Edge Attribute Browser�ǥ��å������פ����Ȥˤ���ǧ���뤳�Ȥ��Ǥ��ޤ������å������뤳�Ȥ�פ��Ф��Ƥ���������Cytoscape�ǥ����ȥåפ�Select��˥塼��ޤ��ǽ�˳���Mouse Drag Selects...�����ޤ���������Cytoscape�Υե��륿�����Ѥ����㤤��������non-core���å������ޤ���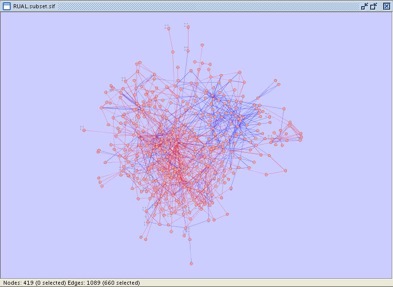
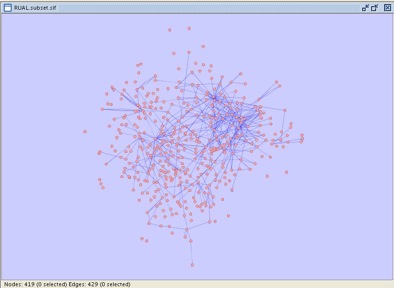
�ǽ�Υͥåȥ������٤�ȥ��å��������äƤ��ޤ������¸�Ū�˳�ǧ���줿��Τ�ʸ���˴�Ť��ƹ⤤�������Τ����ΤϻĤäƤ��ޤ������Ϥμ�ˡ�ˤ�ꡢ���Ŭ�ڤʥ��å��Υ��åȤȤʤ�ޤ������å��Τʤ��Ρ��ɤ�ʣ���Ĥ�ޤ������ե��륿���ǽ�������ʤ�Ǥ��礦�������ǤϤ��ΤҤȤĤ���ˡ���ޤ���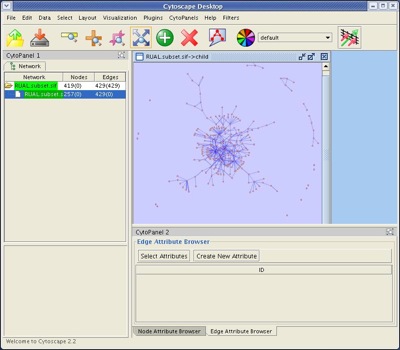
����եΡ��ɤΤߤ���ĥΡ��ɤϽ���Ǥ��ʤ����Ȥ����դ��Ƥ����������������������ϡ��ޥ����ǥ���å����ƴ�ñ�˺���Ǥ��ޤ���
- Cytoscape�Υǥ����ȥåץ�˥塼����Select �� Use Filters�����ޤ���Control Panel���Filters������ɥ��������ޤ���
- Filters������ɥ���ǡ�Options�ɥ��åץ������å���Create new filter�����ޤ�����������New fileter name�ݥåץ��åפ˿������ե��륿����̾�������Ϥ��ޤ�����
- Filter Definition�ե�����ɤǡ��ɥ��åץ�����edge.interaction�����ޤ���Add�ܥ����å����ޤ���
- Advanced�ե���������interaction�ե�����ɤˤƥɥ��åץ�����non_core�����ޤ���Apply��å����ƥե��륿����Ŭ�Ѥ��ޤ�����������Apply�ǤϤʤ�Apply Filter��
- Use Filters������ɥ����Ĥ����������Ȥ����Ĥ���٤�������ɥ��Ϥʤ��ˡ�660���å�������Ƥ��뤳�Ȥ��ǧ���ޤ���������Filters�ΰ��ֲ���Edges��()��ο���660�ȤʤäƤ��ޤ��ˡ�Cytoscape������ɥ��ϲ����Τ褦�ˤʤäƤ���Ǥ��礦��

- Cytoscape�ǥ����ȥåפ�Edit�ˤơ�Delete Selected Nodes/Edges�����ޤ���
- Cytoscape������ɥ��ϲ����Τ褦�ˤʤäƤ���Ǥ��礦��

�ǽ�Υͥåȥ������٤�ȥ��å��������äƤ��ޤ������¸�Ū�˳�ǧ���줿��Τ�ʸ���˴�Ť��ƹ⤤�������Τ����ΤϻĤäƤ��ޤ������Ϥμ�ˡ�ˤ�ꡢ���Ŭ�ڤʥ��å��Υ��åȤȤʤ�ޤ������å��Τʤ��Ρ��ɤ�ʣ���Ĥ�ޤ������ե��륿���ǽ�������ʤ�Ǥ��礦�������ǤϤ��ΤҤȤĤ���ˡ���ޤ���
- �ƥ����Ȥ�°����ߺ��Ѥ˴ؤ��륨�å��Υ����פ�����ե��륿������������磻��ɥ����ɤ� * ����ꤷ�ޤ��������Υե��륿����Ʊ�ͤ���ˡ�Ǻ����Ǥ��ޤ������Advanced�ե���������interaction�ե�����ɤ�non_core������� * �����Ϥ��ޤ������Υե��륿����canvas��Τ��٤ƤΥ��å������ޤ���Apply��������Apply Filter�ˤ�å��������٤ƤΥ��å�������뤳�Ȥ��ǧ���Ƥ���������
- File����New �� Network �� From selected nodes, selected edges�����ޤ�������ˤ��257�Ρ��ɡ�429���å���"child"�ͥåȥ������������ޤ���
- spring-embedded�쥤�����Ȥ�Ŭ�Ѥ��ޤ���������Layout-Cytoscape Layouts-Spring Embedded�ˡ�����ˤ��ʲ��Υͥåȥ������������ޤ���

����եΡ��ɤΤߤ���ĥΡ��ɤϽ���Ǥ��ʤ����Ȥ����դ��Ƥ����������������������ϡ��ޥ����ǥ���å����ƴ�ñ�˺���Ǥ��ޤ���
���ˤϡ��ͥåȥ��������������ۤ�����Ω�Ĥ��Ȥ�����ޤ����Ρ��ɤ䥨�å����ɲä����ꡢ��������ꡣ�㤨�С���ʪ��Ū�ץ��������θ����ͥ��ȹͤ��Ƥ����硢���Υץ������Ǵ��ΤΥ���ѥ��������ꡢ��ʬ�Υǡ������åȤˤϤʤ����Ρ��ɤ��ɲä������ʤ�Ǥ��礦��������Ǥϰʲ��ˤ�����ˡ���ޤ���
- Cytoscape�ǥ����ȥåפκ�¦��Control Panel�ˤ�Editor���֤�å����ޤ���
- Add a Node��̾�դ���줿�Ρ��ɾ�ǥޥ����κ��ܥ����å������ޥ����κ��ܥ�������ޤ�canvas��˥ɥ�å����뤳�Ȥˤ��canvas�˥Ρ��ɤ��ɲä��ޤ���
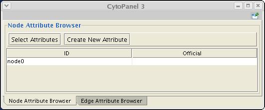
- �ޥ����ǥΡ��ɤ����ޤ���Node Attribute Browser�ˤ�ID��node0�ȤʤäƤ��ޤ����ʲ��˼����ޤ���

- Give your new node a name by going to the Node Attribute Browser�ˤƿ������Ρ��ɤ�̾�����դ��ޤ������ΥΡ��ɤΥ���ȥ��å�����Official HUGO Symbol��̾�դ���줿��ǿ�����̾�������Ϥ��Ƥ����������Ρ��ɤ˿�����ID�����ϤǤ��ʤ����Ȥ����դ��Ƥ�����������������Editor���֤ˤ�Specify Identifier:�˥����å���������ID�����ϲ�ǽ�Ȥʤ�ޤ���
- ���������Ρ��ɤȴ�¸�ΥΡ��ɤ˥��å����ɲä���ˤϰʲ��Τ褦�ˤ��Ƥ�����������������Directed Edge�Ϥʤ���Ctrl�������ʤ���Ρ��ɤ�å�����ȹ�����������¾�ΥΡ��ɤ�å�����ȥ��å��Ȥʤ�ޤ���Esc�����ǹ�����������뤵��ޤ���
- Cytoscape Editor�ˤ�Directed Edge��å����ޤ���
- Directed Edge����ޥ����ܥ�������ޤ�canvas��ο������Ρ��ɤإɥ�å����ޤ������ܥ����Υ����2�ĤΤ�Τ������ޤ����ޥ������Ρ��ɾ�ˤ���Ȥ������������郎���Ρ��ɾ�ǤϤʤ����������������Ȥʤ�ޤ���¾�ΥΡ��ɤ�å��������ĤΥΡ��ɤδ֤˿��������å�������ޤ���
- �������Ρ��ɤȴ�¸�ΥΡ��ɤδ֤ˤ����Ĥ����å����äƤߤƤ���������
- �������Ρ��ɡʤȤ�����դ��Ƥ��륨�å��ˤ�������ˤϥΡ��ɤ�ޥ�����������������Edit��˥塼�����Delete Selected Nodes/Edges�����ޤ����Ρ��ɤ���������硢���μ���Υ��å���������뤳�Ȥ��ǧ���Ƥ���������
- ���ƥ��ꡧ
- ���䡦����
- �Х�������ե��ޥƥ�����

���Υڡ����ؤΥ�����
3nU8DW Really informative article.Thanks Again. Awesome.
7foVBI <a href="http://jkhouiywbtie.com/">jkhouiywbtie</a>, [url=http://srvzpmkbxnfe.com/]srvzpmkbxnfe[/url], [link=http://bqnjtalawzit.com/]bqnjtalawzit[/link], http://boktorcwfhaf.com/
PpiIM3 <a href="http://cstacyvmozcw.com/">cstacyvmozcw</a>, [url=http://jyaxoixdgupp.com/]jyaxoixdgupp[/url], [link=http://tmzughgeflrg.com/]tmzughgeflrg[/link], http://nxztyrornxrb.com/
magnificent points altogether, you simply gained a brand new reader. What would you suggest about your post that you made a few days ago? Any positive? <a href="http://www.deelsonheels.com/$1399__Heel_Cups__Gel_Heel_Pads/p133745_603308.aspx" title="heel pain pads">heel pain pads</a>